导图社区 DNA重组和重组DNA技术
- 172
- 7
- 0
- 举报
DNA重组和重组DNA技术
生物化学与分子生物学之DNA重组和重组DNA技术知识梳理,包括自然界的DNA重组和基因转移、重组DNA技术、重组DNA技术在医学中的应用等等。
编辑于2022-11-02 11:59:48 广东- DNA重组和重组DNA技术
- 相似推荐
- 大纲
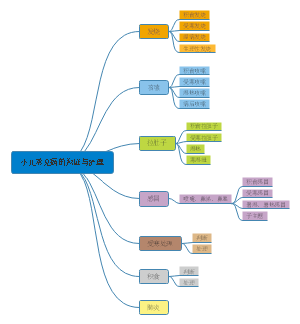
DNA重组和重组DNA技术
概述
DNA重组
包括同源重组、位点特异性重组和转座重组等类型,广泛存在于各类生物,构成了生物的基因变异、物种进化或演变的遗传基础;
是指DNA分子内或分子间发生的遗传信息的重新共价组合过程
重组DNA技术
重组DNA技术可组合不同来源的DNA序列信息,从而创造自然界以前可能从未存在过的遗传修饰生物体,为在分子水平上研究生物奥秘提供了可操作的活体模型。
是指通过体外操作将不同来源的两个或两个以上DNA分子重新组合,并在适当细胞中扩增形成新的功能分子的技术
体外通过人工DNA重组可获得重组体DNA,是基因工程中的关键步骤。
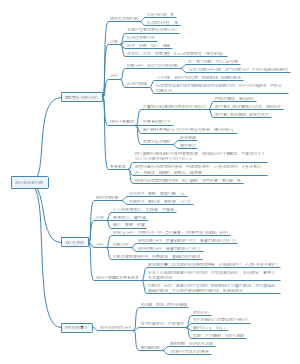
第一节自然界的DNA重组和基因转移
概述
DNA重组
DNA重组是两个或两个以上DNA分子重新组合形成一个DNA分子的过程
自然界DNA重组
自然界不同物种或个体之间的DNA重组和基因转移是经常发生的,这增加了群体的遗传多样性,也通过优化组合积累了有意义的遗传信息。
概念
自然界中的基因转移指DNA片段或基因在不同生物个体或细胞间的传递过程
分类
纵向转移
通过繁殖使DNA或基因在亲代和子代间的传递称作基因纵向转移
横向(水平)转移
打破亲缘关系以直接接触、主动摄取或病毒感染等方式使基因在不同生物个体或细胞间、细胞内不同细胞器间的传递称作基因横向(水平)转移
基因转移
DNA重组和基因转移的方式有多种,包括同源重组、位点特异性重组、转座重组、接合、转化和转导等
其中前三种方式在原核和真核细胞中均可发生,三种方式通常发生在原核细胞。新近研究发现细菌还有一种DNA整合机制,称作成簇规律间隔短回文重复( clustered-regularly- interspaced palindromic repeats, CRISPR)/Cas系统。
一、同源重组是最基本的DNA重组方式
简述
同源重组
在哺乳动物配子发生的减数分裂过程中,同源重组可产生DNA序列的新重组,标示着后代的遗传变异;不种属的细菌和病毒也在水平基因转移中用同源重组互换遗传物质。具有同源序列的两条DNA链通过断裂和再连接引起DNA单链或双链片段的交换。
概念
是指发生在两个相似或相同DNA分子之间核苷酸序列互换的过程,又称基本重组
意义
同源重组的缺陷与人类癌症高度相关
例如,两个相似的抑癌基因 brca1和brca2编码的蛋白质BRCA1和BRCA2与同源重组的发生有关,BRCA2的功能是帮助同源重组的起始,缺乏brca1和brca2的细胞同源重组率减少,对电离辐射的敏感性增加因此,缺乏 brca1和brca2的个体易于患乳腺癌和卵巢癌等。利用同源重组的原理进行基因敲除或基因敲入(也称基因打靶),是将遗传改变引入靶生物体的一种有效方式。为了便于读者理解基本的同源重组原理,下面主要介绍 Holliday模式的同源重组,并以细菌的 RecBCD同源重组作为 Holliday同源重组的例子。
(一)Holliday模型是最经典的同源重组模式
同源重组作为自然界最基本的DNA重组方式,不需要特异DNA序列,而是依赖两分子之间序列的相同或相似性。R. Holliday于1964年提出 Holliday模型,对于认识同源重组起着十分重要的作用。在这一模型中,同源重组主要经历四个关键步骤(图23-1)
关键步骤
两个同源染色体DNA排列整齐;
一个DNA的一条链断裂,与另一个DNA对应链连接,在这个过程中形成了十字形结构,称作 Holliday连接;
通过分支移动产生异源双链DNA),也称 Holliday中间体;
将 Holliday中间体切开并修复,形成两个双链重组体DNA。 Holliday中间体切开方式不同,所得到的重组产物也不同
。如果切开的链与原来断裂的是同一条链,重组体含有一段异源双链区,其两侧来自同一亲本DNA,称为片段重组体( patch recombinant);如果切开的链并非原来断裂的链,重组体异源双链区的两侧来自不同亲本DNA,称为拼接重组体( splice recombinant)。
图片
(二) RecBCD模式是大肠埃希菌的 Holliday同源重组
目前对大肠埃希菌(E. coli)的DNA同源重组分子机制了解最清楚。参与细菌DNA同源重组的酶有数十种,其中最关键的是RecA蛋白、 RecBCD复合物和RuvC蛋白。
1.参与细菌 RecBCD同源重组的酶
细菌的 RecBCD同源重组由以下酶和酶复合物催化完成
(1)RecBCD复合物 ;
具备的三种酶活性
依赖ATP的核酸外切酶活性
可被ATP增强的核酸内切酶活性
需要ATP的解旋酶活性
作用机制
RecBCD复合物利用ATP水解提供能量,沿着DNA链运动,并以较快的速度将前方DNA解旋
当遇到Chi位点(5’-GCTGGTGG-3’)时,可在其下游切出3’-端的游离单链,从而使DNA重组成为可能。
chi(因交换位点的DNA结构类似于希腊字母X而得名)
(2)RecA蛋白
作用
RecA蛋白可结合单链DNA( ssDNA),形成 RecA-ssDNA复合物
在有同源DNA存在时,此复合物可与含同源序列的靶双链DNA相互作用,并将结合的单链DNA插入双链DNA的同源区,与互补链配对,而将同源链置换出来
(3)RuvC蛋白
作用
RuvC蛋白有核酸内切酶活性,能专一性识别 Holliday连接点,并有选择地切开同源重组体的中间体
2.E.coli的 RecBCD同源重组过程
E.coli的 RecBCD同源重组过程如图23-2
RecBCD复合物识别双链断裂的断裂口平端或近似平端,然后向上游边移行边解链
当遇到Chi位点时,在3’-单链上切开产生单链切口
RecA蛋白催化3’-单链DNA另一双链DNA的侵入,并与其中的一条链交叉,继而交叉分支移动
待相交的另一链在 RecBCD内切酶活性催化下断裂后,由DNA连接酶交换连接缺失的远末端,形成Holliday中间体
此中间体再经RuvC切割和DNA连接酶的连接,最后完成重组
图解
二、位点特异性重组是发生在特异位点间的DNA整合
该类重组广泛存在于各类细胞中,起着十分重要的作用,如某些基因表达的调节、发育过程中程序性DNA重排以及有些病毒和质粒DNA复制循环过程中发生的整合和切除等。以下是位点特异性重组的例子。
简述
位点特异性重组
概念
位点特异性重组是发生在至少拥有一定程度序列同源性片段间DNA链的互换过程,也称保守的位点特异性重组
位点特异性重组酶SSR)通过识别和结合DNA短序列(位点)使DNA片段发生重排
(一)λ噬菌体DNA可与宿主染色体DNA发生整合
作用机制
λ噬菌体DNA的整合是在λ噬菌体的整合酶催化下完成的,是λ噬菌体DNA与宿主染色体DNA特异靶位点之间的选择性整合
λ噬菌体DNA的重组位点att P与大肠埃希菌基因组DNA的重组位点att B之间有15bp核心序列相同,在整合酶(Int)和整合宿主因子(IHF)作用下可发生整合,由Xis参与切除过程。通常这种由整合酶催化的DNA整合是十分特异而有效的。逆转录病毒整合酶可特异地识别、整合逆转录病毒cDNA的长末端重复序列(long terminal repeat, LTR)。
图片
(图23-3)
(二)基因片段倒位是细菌位点特异性重组的一种方式
鞭毛相转变
在单菌落的沙门菌中经常出现少数另一种含H抗原的细菌,这种现象称为鞭毛相转变
遗传分析表明,这种抗原相位的改变是由基因中一段995bp的H片段发生倒位所致
以鼠伤寒沙门菌H抗原编码基因中H片段重组为例。鼠伤沙门菌的H抗原有两种,分别为H1和H2鞭毛蛋白。在单菌落的沙门菌中经常出现少数另一种含H抗原的细菌,这种现象称为鞭毛相转变。遗传分析表明,这种抗原相位的改变是由基因中一段995bp的H片段发生倒位所致。如图23-4所示,H片段的两端为14bp的特异性重组位点(hix),其方向相反,发生重组后可使H片段倒位。H片段上有两个启动子(P),其一驱动hin基因表达,另一个驱动H2和rH1基因表达,倒位后H2和rH1基因不表达。hin基因编码特异的重组酶,即倒转酶( invertase)Hin,该酶为同源二聚体,分别结合在两个hix位点上,并由辅因子Fis( factor for inversion stimulation)促使DNA弯曲而将两个hix位点连接在一起,DNA片段经断裂和再连接而发生倒位。rH1表达产物为H1阻遏蛋白,当H2基因表达时,rH1也表达,从而使H1基因被阻遏;反之,H2基因不表达时,rH1也不表达,H1基因阻遏被解除。
图片
(三)免疫球蛋白基因以位点特异性重组发生重排
免疫球蛋白编码基因V-(D)-J重排及T细胞受体基因V-(D)-J重排都是利用位点特异性重组的原理。
三、转座重组可使基因位移
转座重组概念
转座重组或转座是指由插入序列和转座子介导的基因移位或重排。
(一)插入序列是最简单的转座元件
插入序列
通常是转座子的一种,只携带与自身转座有关的编码基因。 典型的IS两端各一个9~41bp的反向重复序列,反向重复序列侧翼连接有短的(4~12bp)、不同的IS所特有的正向重复序列。
概念
插入序列( IS)是指能在基因(组)内部或基因(组)间改变自身位置的一段DNA序列
独特的结构特征
两端是反向重复序列(IR)
中间是一个转座编码基因
表达产物可引起IS转座
不同形式分类
保守性转座
IS从原位迁至新位
(P425图23-5)
图片
复制性转座
IS复制后的一个复制本迁至新位
(二)转座子可以在染色体间转座
转座子
一般属于复合型转座子( composite Tn),即有一个中心区域,两边侧翼序列是插入序列(IS),除有与转座有关的编码因外,还携带其他基因如抗生素抗性基因等(图23-6)。Tn普遍存在于原核和真核细胞中,不但可以在一条染色体上移动,也可以从一条染色体跳到另一条染色体上,甚至从一个细胞进入另一个细胞。Tn在移动过程中,DNA链经历断裂及再连接的过程,可能导致某些基因开启或关闭,引起插入突变、新基因生成、染色体畸变及生物进化。
转座子(Tn)是指能将自身或其拷贝插入基因组新位置的DNA序列
图片
四、原核细胞可通过接合、转化和转导进行基因转移或重组
原核细胞(如细菌)可通过细胞间直接接触(接合作用)、细胞主动摄取(转化作用)或噬菌体传递(转导作用)等方式进行基因转移或重组。
(一)接合作用是质粒DNA通过细胞间相互接触发生转移的现象
接合作用
接合作用是指细菌的遗传物质在细菌细胞间通过细胞-细胞直接接触或细胞间桥样连接的转移过程。
当细菌通过鞭毛相互接触时,质粒DNA就可以从一个细菌转移至另一细菌,但并非任何质粒DNA都有这种转移能力,只有某些较大的质粒,如F因子(F factor),方可通过接合作用从一个细胞转移至另一个细胞。F因子决定细菌表面鞭毛的形成,当含有F因子的细菌(F+细菌)与没有F因子的细菌(F-细菌)相遇时,在两细菌间形成性鞭毛连接桥,接着质粒双链DNA中的一条链会被酶切割,产生单链切口,有切口的单链DNA通过鞭毛连接桥向F-细胞转移,随后,在两细胞内分别以单链DNA为模板合成互补链。
(二)转化作用是受体细胞自主摄取外源DNA并与之整合的现象
转化作用
受体菌必须处于敏化状态,这种敏化状态可以通过自然饥饿、生长密度或实验室诱导而达到。例如,当溶菌时,裂解的DNA片段作为外源DNA被另一细菌(受体菌)摄取,受体菌通过重组机制将外源DNA整合至其基因组上,从而获得新的遗传性状,这就是自然界发生的转化作用。然而,由于较大的外源DNA不易透过细胞膜,因此,自然界发生转化作用的效率并不高,染色体整合概率则更低。
转化作用是指受体菌通过细胞膜直接从周围环境中摄取并掺入外源遗传物质引起自身遗传改变的过程
(三)转导作用是病毒将供体DNA带入受体并与之染色体发生整合的现象
转到作用
自然界中常见的例子是噬菌体介导的转导,包括普遍性转导( generalized transduction)和特异性转导(specialized transduction),后者又称为限制性转导( restricted transduction)。
转导作用是指由病毒或病毒载体介导外源DNA进入靶细胞的过程
分类
1.普遍性转导的基本过程
当噬菌体在供体菌内包装时,供体菌自身的DNA片段被包装入噬菌体颗粒
随后细菌溶解,所释放出来的噬菌体通过感染受体菌而将所携带的供体菌DNA片段转移至受体菌中
进而重组于受体菌的染色体DNA上
2.特异性转导的基本过程
当噬菌体感染供体菌后,噬菌体DNA以位点特异性重组机制整合于供体菌染色体DNA上
当整合的噬菌体DNA从供体菌染色体DNA上切离时,可携带位于整合位点侧翼的DNA片段
随后切离出来的噬菌体DNA被包装入噬菌体衣壳中
供体菌裂解,所释放出来的噬菌体感染受体菌
携带有供体菌DNA片段的噬菌体DNA整合于受体菌染色体DNA的特异性位点上
位于整合位点侧翼的供体菌DNA片段重组至受体菌染色体DNA上
五、细菌可通过 CRISPR/Cas系统从病毒获得DNA片段作为获得性免疫机制
CRISPR/Cas系统(CRISPR/Cas system)是原核生物的一种获得性免疫系统,用于抵抗存在于噬菌体或质粒的外源遗传元件的入侵。关于细菌的 CRISPR/Cas系统的发现过程可参看数字扩展相关内容。
(一)CRISPR序列的结构特征
CRISPR存在于已测序的40%细菌基因组和90%古细菌( archaea)基因组中
成簇规律间隔短回文重复(CRISPR)
是指细菌基因组上成簇排列的、由来自噬菌体DNA的间隔序列和宿主菌基因组的重组序列所形成的特殊重复序列-间隔序列阵列
与Cas基因( Cas gene)相邻 (P426图23-7)
(二)外源DNA可插入宿主基因组的 CRISPR座
过程
以噬菌体感染为例
当噬菌体感染宿主菌后,噬菌体DNA进入宿主细胞并复制,复制所产生的DNA片段可以被宿主细胞的Cas1-Cas2复合物捕获
然后,Cas1-cas2复合物将所捕获的DNA片段插入到宿主基因组 CRISPR座位的第一个位点,
Cas1在此过程中协调切割连接反应,即在重复序列5’-端切开,然后与DNA片段的3’-端连接
(P427图23-8)
这种机制在跨越插入的DNA片段两端的重复序列上产生两个单链DNA缺口,最后由DNA聚合酶将缺口封闭
图片
(三)CRISPR/Cas系统是细菌的获得性免疫机制
CRISPR/Cas9系统是一种细菌防御病毒和质粒攻击的获得性免疫机制,目前已经被开发成一种应用最多的高效率、低脱靶率的基因组编辑( genome editing)技术。
CRISPR/Cas系统
概念
CRISPR/Cas系统是指由Cas基因编码的Cas蛋白催化 CRISPR形成,以及 CRISPR转录产物与Cas蛋白相配合介导入侵DNA切割的机制,并成为细菌抵抗病毒感染的一种获得性免疫机制
分型
根据Cas蛋白的功能可将其分为三型,即Ⅰ型、Ⅱ型和Ⅲ型
其中Ⅱ型 CRISPR/Cas9系统是目前应用最多的。
工作原理
以Ⅱ型 CRISPR/Cas9系统为例介绍 CRISPR/Cas系统的工作原理(P428图23-9)
Ⅱ型系统中由重复序列及间隔序列组成的CRISPR座位经转录产生 CRISPR-RNA前体和 tracrRNA
tracrRNA与pre-crRNA的重复序列区互补配对产生局部双链RNA( dsRNA)
RNaseⅢ识别并切割 dsRNA产生向导crRNA( gcrRNA)
宿主细胞表达的Cas9核酸酶与 gcrRNA结合形成Cas9-crRNA复合物
当含有相同间隔序列的噬菌体或质粒再次入侵时,Cas9- crRNA复合物与入侵DNA上的原间隔序列互补配对形成由 protospacer/crRNA组成的R-环双链结构
Cas9识别并切割R-环,从而在入侵者的基因组上产生切口
Cas9切割的靶序列下游有一个紧邻原间隔序列基序(PAM),可能对于Cas9寻找靶序列有一定作用
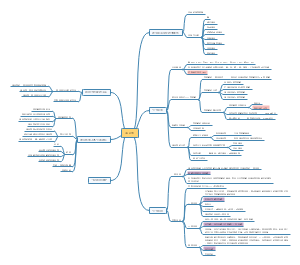
第二节重组DNA技术
概述
重组DNA技术
在克隆目的基因后,还可针对该基因进行表达产物蛋白质或多肽的制备以及基因结构的定向改造。自1972年成功构建第一个重组DNA分子以来,重组DNA技术得到了快速发展,人们几乎可以随心所欲地分离、分析、切割-连接等操作基因。另外,该技术在生物制药基因诊断、基因治疗等诸多方面都得到了广泛应用。
概念
重组DNA技术又称分子克隆、DNA克隆或基因工程,是指通过体外操作将不同来源的两个或两个以上DNA分子重新组合,并在适当细胞中扩增形成新功能DNA分子的方法
主要过程
在体外将目的DNA片段
与能自主复制的遗传元件(又称载体)连接形成重组DNA分子
进而在受体细胞中复制、扩增及克隆化
从而获得单DNA分子的大量拷贝
一、重组DNA技术中常用的工具酶
在重组DNA技术中,常需要一些工具酶用于基因的操作。例如,对目的DNA( target DNA)进行处理时,需利用序列特异性限制性核酸内切酶( restriction endonuclease,RE),RE在准确的位置切割DNA,使较大的DNA分子成为一定大小的DNA片;构建重组DNA分子时,必须在DNA连接酶催化下才能使DNA片段与载体共价连接。此外,还有一些工具酶也是重组DNA时所必不可少的。
(一)常用工具酶具有各自功能
为了方便快速浏览重组DNA技术中一些常用工具酶及其基本功能,我们将一些常用工具酶概括于表23-1。
(二)限制性核酸内切酶是最重要的工具酶
在所有工具酶中,RE具有特别重要的地位,因此,有关RE的内容单独介绍。
简述
限制性核酸内切酶(RE)
概念
简称为限制性内切酶或限制酶,是一类核酸内切酶,能识别双链DNA分子内部的特异序列并裂解磷酸二酯键
来源
除极少数RE来自绿藻外,绝大多数来自细菌,与相伴存在的甲基化酶共同构成细菌的限制修饰体系
作用
RE对甲基化的自身DNA分子不起作用,仅对外源DNA切割,因此对细菌遗传性状的稳定具有重要意义
1.RE的分类及其特点
目前发现的RE有6000多种。根据RE的组成所需因子及裂解DNA方式的不同可分为三种类型,即I、Ⅱ和Ⅲ型。
I型和Ⅲ酶为复合功能酶,同时具有限制和DNA修饰两种作用,且不在所识别的位点切割DNA(即特异性不强);
Ⅱ型酶能在DNA双链内部的特异位点识别并切割,故其被广泛用作“分子剪刀”,对DNA进行精确切割。
因此,重组DNA技术中所说的RE通常指Ⅱ型酶。
2.RE的命名原则
RE的命名 Smith采用和 Nathane提出的属名与种名相结合的命名法
即第一个字母是酶来源的细菌属名的首字母,用大写斜体;第二、三个字母是细菌菌种名的首字母,用小写斜体;第四个字母(有时无)表示细菌的特定菌株,用大写或小写;罗马数字表示RE在此菌种发现的先后顺序。例如,EcoR I:E= Escherichia,埃希菌属;co=coli,大肠杆菌菌种;R=RY3,菌株名;I,为从此菌中第一个分离获得的RE。
3.RE识别及切割特异DNA序列
Ⅱ型RE的识别位点通常为6或4个碱基序列,个别的RE识别8或8个以上碱基序列
P429表23-2列举了部分Ⅱ型RE的识别位点
大多数RE的识别序列为回文序列
回文结构是指在两条核苷酸链的特定位点,从5’→3’方向的序列完全一致
例如, EcoR I的识别序列,在两条链上的5’→3’序列均为GAATTC。
4.RE中的同尾酶
同尾酶
有些RE所识别的序列虽然不完全相同,但切割DNA双链后可产生相同的单链末端(黏端),这样的酶彼此互称同尾酶
所产生的相同黏端称为配伍末端
例如,BamH I(G’GATCC)和Bgl(A’GATCT)在切割不同序列后可产生相同的5’黏端,即配伍末端(—GATC一)。配伍末端可共价连接,但连接后的序列通常就不能再被两个同尾酶中的任何一个酶识别和切割了。
5.RE中的同裂酶
有些RE虽然来源不同,能识别同一序列(切割位点可相同或不同),这样的两种酶称同切点酶或异源同工酶
例如, BamH和BstI能识别并在相同位点切割同一DNA序列(G’GATCC);Xma I和Sma I虽能识别相同序列( GGGCCC),但切割位点不同,前者的切点在识别序列的第一个核苷酸后(G’GGCCC),而后者的切点则在序列的中间( GGG’CCC)。同
切点酶为DNA操作者增加了酶的选择余地。
二、重组DNA技术中常用的载体
载体( vector)是为携带目的外源DNA片段、实现外源DNA在受体细胞中无性繁殖或表达蛋白质所采用的一些DNA分子,按其功能可分为克隆载体和表达载体两大类,有的载体兼有克隆和表达两种功能。
(一)克隆载体用于扩增克隆化DNA分子
克隆载体简述
克隆载体是指用于外源DNA片段的克隆和在受体细胞中扩增的DNA分子
基本特点
至少有一个复制起点使载体能在宿主细胞中自主复制,并能使党隆的外源DNA片段得到同步扩增;
至少有一个选择标志,从而区分含有载体和不含有载体的细胞,
如抗生素抗性基因、β-半乳糖苷酶基因、营养缺陷耐受基因等;
有适宜的RE单一切点,可供外源基因插入载体。常用克隆载体主要有质粒、噬菌体DNA等
1.质粒克隆载体
质粒克隆载体是重组DNA技术中最常用的载体,可以是天然质粒,更多是人工改造的质粒
质粒是细菌染色体外的、能自主复制和稳定遗传的双链环状DNA分子,具备作为克隆载体的基本特点
例如,pUC18质粒载体,具有一个复制起点ori,一个选择标志——氨苄青霉素抗性基因ampR,多个单一酶切位点,也称多克隆酶切位点( multiple cloning sites,MCS)(图23-10)
2.噬菌体DNA载体
λ和M13噬菌体DNA常用作克隆载体
稍早经λ噬菌体DNA改造的载体系统有λgt系列和EMBL系列
λgt系列(插入型载体,适用于cDNA克隆)和EMBL系列(置换型载体,适用于基因组DNA克隆)
经改造的M13载体有M13mp系列和pUC系列
它们是在M13的基因间隔区插入了大肠埃希菌(E.coli)的一段调节基因及β-半乳糖苷酶(lacZ)N-端146个氨基酸残基编码基因,其编码产物为β-半乳糖苷酶的α片段
α互补
突变的E.coli宿主(lac-)仅表达该酶的ω片段(酶的C-端)。单独存在β-半乳糖苷酶的α片段或ω片段都没有酶的活性,只有携带α片段基因的M13进入宿主细胞,宿主细胞才能同时表达α和ω片段,产生有活性的β-半乳糖苷酶,使特异性底物变为蓝色化合物,这就是所谓的α互补(α complementation)
蓝白筛选
当外源基因的插位点设计在LacZ基因内部时,外源基因的插入则会干扰LacZ的表达,利用lacZ-菌株为宿主细胞,在含LacZ底物X-gal和诱导剂IPTG的培养基上生长时会出现白色菌落;如果在lacZ基因内无外源基因插入,则有LacZ表达,转化菌在同样条件下呈蓝色菌落,这就是蓝白筛选。很多质粒载体也构建了蓝白筛选系统
3.其他克隆载体
为增加克隆载体携带较长外源基因的能力,还设计有柯斯质粒载体(又称黏粒载体)、细菌人工染色体(BAC)载体和酵母人工染色体(YAC)载体等
柯斯质粒是人工构建的含λ DNA Cos序列和质粒复制子的特殊类型质粒载体,自身分子量一般只有5~7kb,但能携带的外源DNA片段最大可达45kb。BAC是以大肠埃希菌性因子F质粒为基础构建的克隆载体,可携带的外源DNA片段在50~300kb之间。YAC是含酵母染色体上必需的端粒、着丝点和复制起始序列的人工构建载体,能携带400kb左右的DNA片段。
(二)表达载体能为外源基因提供表达元件
下面简介原核表达载体和真核表达载体的结构特点
简述
表达载体
概念
表达载体是指用来在宿主细胞中表达外源基因的载体
分类
依据其宿主细胞的不同可分为原核表达载体和真核表达载体
它们的区别主要在于为外源基因提供的表达元件
工作原理
利用表达载体提供的表达元件也可在体外建立无细胞表达体
根据表达载体上的表达元件决定提供原核细胞提取物或真核细胞提取物,其基本工作原理相同于在细胞内
1.原核表达载体
简述
该类载体用于在原核细胞中表达外源基因,由克隆载体发展而来,除了具有克隆载体的基本特征外,还有供外源基因有效转录和翻译的原核表达调控序列
如启动子核糖体结合位点即SD序列( Shine-Dalgarno- sequence)、转录终止序列等。原核表达载体的基本组成如图23-11所示。目前应用最广泛的原核表达载体是E.coli表达载体
2.真核表达载体
简述
该类载体用于在真核细胞中表达外源基因,也是由克隆载体发展而来的,除了具备克隆载体的基本特征外,所提供给外源基因的表达元件是来自真核细胞的。
特点
含有必不可少的原核序列,如复制起点、抗生素抗性基因、多克隆酶切位点(MCS)等,用于真核表达载体在细菌中复制及阳性克隆的筛选;
真核表达调控元件,如真核启动子、增强子、转录终止序列、poly(A)加尾信号等;
真核细胞复制起始序列,用于载体或基因表达框架在真核细胞中的复制;
真核细胞药物抗性基因,用于载体在真核细胞中的阳性筛选巴。
P432图23-12显示的是真核表达载体的基本组成。根据真核宿主细胞的不同,真核表达载体可分为酵母表达载体昆虫表达载体和哺乳类细胞表达载体等。
三、重组DNA技术的基本原理及操作步骤
完整DNA克隆过程包括五大步骤
(P432图23-13)
目的DNA的分离获取(分);
载体的选择与准备(选);
目的DNA与载体的连接(连);
重组DNA转入受体细胞(转);
重组体的筛选及鉴定(筛)。
(一)目的DNA的分离获取是DNA克隆的第一步
分离获取目的DNA的方法主要有以下几种:
方法
1.化学合成法
该方法可直接合成目的DNA片段,通常用于小分子肽类基因的合成
其前提是已知某基因的核苷酸序列,或能根据氨基酸序列推导出相应核苷酸序列
一般先合成两条完全互补的单链,经退火形成双链,然后克隆于载体
2.从基因组文库和CDNA文库中获取目的DNA
关于两种文库的构建和从文库中筛选目的DNA/cDNA的方法已经基本商业化了,可以根据具体需求从公司订购。
3.PCR法
PCR是一种高效特异的体外扩增DNA的方法
(见第二十四章)
使用PCR法的前提是:已知待扩增目的基因或DNA片段两端的序列,并根据该序列合成适当引物
4.其他方法
除上述方法外,也可采用酵母单杂交系统克隆DNA结合蛋白的编码基因,或用酵母双杂交系统克隆特异性相互作用蛋白质的编码基因。
(二)载体的选择与准备是根据目的DNA片段决定的
DNA克隆的目的
一是获取目的DNA片段
针对第一种目的,通常选用克隆载体
二是获取目的DNA片段所编码的蛋白质
针对第二种目的,需选择表达载体
选择载体时还要考虑目的DNA的大小、受体细胞的种类和来源等因素
(表23-3)。除了上述需要考虑的因素外,选择载体时还需要注意载体内应有适宜的单一酶切位点或MCS,以便根据目的DNA片段,对载体进行适当的酶切处理。总之,在重组DNA技术中,载体的选择、准备和改进极富技术性,目的不同,操作基因的性质不同,载体的选择和改建方法也不同。
(三)目的DNA与载体连接形成重组DNA
依据目的DNA和线性化载体末端的特点,可采用不同的连接策略。主要连接策略如下:
1.黏端连接
依靠酶切后的黏性末端进行连接,不仅连接效率高,也具有方向性和准确性。根据酶切策略不同可有以下几种黏端连接策略。
(1)单一相同黏端连接
产生机制
如果目的DNA序列两端和线性化载体两端为同一RE(或同切点酶,或同尾酶)切割所致,那么所产生的黏端完全相同
连接结果
这种单一相同黏端连接时会有三种连接结果:
载体自连(载体自身环化)
载体与目的DNA连接
DNA片段自连
缺点
从而给后续筛选增加了困难
容易出现载体自身环化
采用碱性磷酸酶预处理线性化载体DNA,使之去磷酸化,可有效减少载体自身环化
目的DNA可以双向插入载体(即正向和反向插入)
目的DNA如果反向插入载体,虽然不影响基因克隆,但却影响外源基因的表达。
多拷贝连接现象
(2)不同黏端连接
产生机制
如果用两种不同的RE分别切割载体和目的DNA,则可使载体和目的DNA的两端均形成两个不同的黏端,这样可以让外源DNA定向插入载体
定向克隆
定向克隆也可通过一端为平端,另一端为黏端的连接方法来实现。定向克隆可有效避免载体自连和DNA片段的反向插入和多拷贝现象。
这种使目的基因按特定方向插入载体的克隆方法称为定向克隆
(3)通过其他措施产生黏端的连接
:常用的在末端为平端的目的DNA片段制造黏端的方法有:
1、人工接头法
用化学合成法获得含RE位点的平端双链寡核苷酸接头,将此接头连接在目的DNA的平端上
然后用相同的RE切割人工接头产生黏端,进而连接到载体上
2、加同聚物尾法
用末端转移酶将某一核苷酸(如dC)逐一加到目的DNA的3’-端羟基上,形成同聚物尾(如同聚dC尾)
同时又将与之互补的另一核苷酸(如dG)加到载体DNA的3’-端羟基上,形成与目的DNA末端互补的同聚物尾(如同聚dG尾)
两个互补的同聚物尾均为黏端,因而可高效率地连接到一起
3、PCR法
针对目的DNA的5’-端和3’-端设计一对特异引物,在每条引物的5’端分别加上不同的RE位点
然后以目的DNA为模板,经PCR扩增便可得到带有引物序列的目的DNA
再用相应RE切割PCR产物,产生黏端,随后便可与带有相同黏端的线性化载体进行有效连接。
T-A克隆
在使用 Taq DNA聚合酶进行PCR时,扩增产物的3′-端一般多出一个不配对的腺苷酸残基(A)而成为黏端,这样的PCR产物可直接与3’-端带不配对的胸腺嘧啶残基(T)的线性化载体(T载体)连接,此即T-A克隆。
2.平端连接
若目的DNA两端和线性化载体两端均为平端,则两者之间也可在DNA连接酶的作用下进行连接
其连接结果有三种:载体自连、载体与目的DNA连接和DNA片段自连,但连接效率都较低
为了提高连接效率,可采用提高连接酶用量延长连接时间降低反应温度、增加DNA片段与载体的摩尔比等措施。
平端连接同样存在载体自身环化、目的DNA双向插入和多拷贝现象等缺点
3.黏-平端连接
黏-平末端连接是指目的DNA和载体通过一端为黏端、另一端为平端的方式进行连接。
以该方式连接时,目的DNA被定向插入载体(定向克隆),连接效率介于黏端和平端连接之间
可采用提高平端连接效率的措施提高该方式的连接效率。
(四)重组DNA转入受体细胞使其得以扩增
工程细胞
概念
理想的宿主细胞通常是DNA/蛋白质降解系统和(或)重组酶缺陷株,这样的宿主细胞称为工程细胞。
特点
工程细胞具有较强的接纳外源DNA的能力,可保证外源DNA长期、稳定地遗传或表达
导入方式
将重组DNA导入宿主细胞的常用方法有如下几种:
1.转化
概念
转化是指将外源DNA直接导入细菌、真菌的过程
例如,重组质粒导大肠埃希菌。
此外,将质粒DNA直接导入酵母细胞以及将黏粒DNA导入细菌的过程也称作转化
感受态细胞
只有细胞膜通透性增加的细菌才容易接受外源DNA,这样的细菌称作感受态细胞
实现方法
化学诱导法(如氯化钙法)、电穿孔法等
2.转染
概念
转染是指将外源DNA直接导入真核细胞(酵母除外)的过程
此外,将噬菌体DNA直接导入受体细菌的过程也称作转染
常用方法
常用的转染方法包括化学方法(如磷酸钙共沉淀法、脂质体融合法等)和物理方法(如显微注射法、电穿孔法等)
3.感染
概念
感染是指以病毒颗粒作为外源DNA运载体导入宿主细胞的过程
例如,以噬菌体、逆转录病毒、腺病毒等DNA作为载体构建的重组DNA分子,经包装形成病毒颗粒后进入宿主细胞。
(五)重组体的筛选与鉴定
筛选与鉴定方法
重组DNA分子导入宿主细胞后,可通过载体携带的选择标记或目的DNA片段的序列特征进行筛选和鉴定,从而获得含重组DNA分子的宿主细胞。
1.借助载体上的遗传标志进行筛选
载体上通常携带可供重组体筛选的遗传标志,如抗生素抗性基因等,据此可对含重组DNA的宿主细胞进行筛选。
分类
(1)利用抗生素抗性标志筛选:
将含有某种抗生素抗性基因的重组载体转化宿主细胞,然后在含相应抗生素的培养液中培养此细胞,若细胞能在这种条件下生长,则说明细胞中至少应含有导入的载体,但是否是插入目的DNA的载体,还需要进一步鉴定。若细胞中没有载体,则被抗生素杀死。
(2)利用基因的插入失活/插入表达特性筛选:
针对某些带有抗生素抗性基因的载体,当目的DNA插入抗性基因后,可使该抗性基因失活。如果还以这种抗生素抗性进行筛选,不能生长的细胞应该是含重组DNA的细胞。以这种方式筛选时,通常载体上携带一个以上筛选标志基因。例如pBR322质粒含有氨苄青霉素抗性基因(ampR)和四环素抗性基因(tetR),如将目的DNA插入tetR中,tetR失活,含重组DNA的细胞只能在含氨苄青霉素的培养基中生长,而不能在含四环素的培养基中生长(P434图23-14)。
(3)利用标志补救筛选:
标志补救( marker rescue)是指当载体上的标志基因在宿主细胞中表达时,宿主细胞通过与标志基因表达产物互补弥补自身的相应缺陷,从而在相应选择培养基中存活。利用该策略可初步筛选含有载体的宿主细胞。例如,S. cerevisiae酵母菌株,因trp1基因突变而不能在缺少色氨酸的培养基上生长,当转入带有功能性trp1基因的重组载体后,转化菌则能在色氨酸缺陷的培养基上生长。标志补救也可用于外源基因导入哺乳类细胞后阳性克隆的初筛,例如,当将带有二氢叶酸还原酶(DHFR)基因(dhfr)的真核表达载体导入dhfr缺陷的哺乳类细胞后,则可使细胞在无胸腺嘧啶的培养基中存活,从而筛选出带有载体的克隆(DHFR可催化二氢叶酸还原成四氢叶酸,者可用于合成胸腺嘧啶)。 利用α互补筛选携带重组质粒的细菌也是一种标志补救筛选方法。关于α互补原理在本节“重组DNA技术中常用载体”部分已有介绍,在此仅以图23-15概括说明将外源基因插入载体lacZ基因N-端序列时是如何进行筛选的。
(4)利用噬菌体的包装特性进行筛选
:λ噬菌体的一个重要遗传特性就是其在包装时对λDNA大小有严格要求,只有当入λDNA的长度达到其野生型长度的75%~105%时,方能包装形成有活性的噬菌体颗粒,进而在培养基上生长时呈现清晰的噬斑,而不含外源DNA的单一噬菌体载体DNA因其长度太小而不能被包装成有活性的噬菌体颗粒,故不能感染细菌形成噬斑。根据此原理可初步筛出带有重组λ噬菌体载体的克隆。
2.序列特异性筛选
根据序列特异性筛选的方法包括RE酶切法、PCR法、核酸杂交法、DNA测序法等。
(1)RE酶切法
针对初筛为阳性的克隆,提取其重组DNA,以合适的RE进行酶切消化,经琼脂糖凝胶电泳便可判断有无目的DNA片段的插入及插入片段的大小
同时,根据酶切位点在插入片段内部的不对称分布,还可鉴定插入DNA片段在载体上的方向
也可用多种RE制作并分析插入片段的酶切图谱
(2)PCR法
利用序列特异性引物,经PCR扩增,可鉴定出含有目的DNA的阳性克隆。
如果利用克隆位点两侧载体序列设计引物进行PCR扩增,再结合序列分析,便能可靠地证实插入片段的方向、序列和可读框的正确性。
(3)核酸杂交法:
常用方法是菌落或噬斑原位杂交法,其基本过程如P436图23-16所示:将转有外源DNA的菌落或噬斑影印到硝酸纤维素膜上,细菌裂解后所释放出的DNA将被吸附在膜上,将膜与标记的核酸探针杂交,通过检测探针的存在即可鉴定出含有重组DNA的克隆。根据核酸探针标记物的不同,可通过放射自显影、化学发光、酶作用于底物显色等方法来显示探针的存在位置,也就是阳性克隆存在的位置。
该方法可直接筛选和鉴定含有目DNA的克隆。
(4)DNA测序法
该法是最准确的鉴定目的DN的方法
针对已知序列,通过DNA测序可明确具体序列和可读框的正确性;针对未知DNA片段可揭示其序列,为进一步研究提供依据。
3.亲和筛选法
亲和筛选法的前提是重组DNA进入宿主细胞后能够表达出其编码产物。
常用的亲和筛选法的原理是基于抗原抗体反应或配体受体反应
一般做法与上述菌落或噬斑核酸原位杂交相似,只是被检测的靶分子换成吸附于硝酸纤维素膜上的蛋白质,检测探针换成标记的抗体/抗原或配体/受体。
(六)克隆基因的表达
采用重组DNA技术还可进行目的基因的表达,实现生命科学研究、医药或商业目的,这是基因工程的最终目标。基因表达涉及正确的基因转录、mRNA翻译、适当的转录后及翻译后的加工过程,这些过程对于不同的表达体系是不同的。克隆目的基因,进而大量地表达出有特殊意义的蛋白质,已成为重组DNA技术中一个专门的领域,这就是重组蛋白质表达。在蛋白质表达领域,表达体系的建立包括表达载体的构建、宿主细胞的建立及表达产物的分离、纯化等技术和策略。基因工程中的表达系统包括原核和真核表达体系。
1.原核表达体系
E.coli是当前采用最多的原核表达体系,其优点是培养方法简单、迅速、经济而又适合大规模生产工艺。
(1)原核表达载体的必备条件
运用E.coli表达有用的蛋白质必须使构建的表达载体符合下述标准
含E.coli适宜的选择标志;
具有能调控转录、产生大量mRNA的强启动子;
如lac、tac启动子或其他启动子序列;
含适当的翻译控制序列,如核糖体结合位点和翻译起始点等;
含有合理设计的MCS,以确保目的基因按一定方向与载体正确连接
。关于原核表达载体的基本组成见P431图23-11。
(2)重组蛋白质的表达策略
在实际工作中蛋白质表达策略颇不一致
有时表达目的是为了获得蛋白质抗原,以便制备抗体,此时要求表达的蛋白质或多肽具有抗原性,同时要求表达产物易于分离、纯化。较好的策略是为目的基因连上一个编码标签肽的序列,从而表达为融合蛋白( fusion protein)。在有些情况下,表达的蛋白质多为不溶性的包含体( inclusion body),极易与细菌蛋白质分离。如果在设计融合基因时,在目的基因和标签序列之间加入适当的裂解位点,则很容易从表达的融合分子中去除标签序列。巧妙地设计标签序列还可大大方便表达产物的分离纯化。如果表达的蛋白质是为了用于生物化学、细胞生物学研究或临床诊断或基因防治,除分离纯化方便,更重要的是考虑蛋白质的功能和生物学活性。此时,表达可溶性蛋白质往往具有特异的生物学功能;如果表达的是包含体形式,还需要在分离纯化后进行复性或折叠。
(3)E.coli表达体系的缺点
E.coli表达体系在实际应用中尚存在一些不足之处,诸如
由于缺乏转录后加工机制,对于真核基因来说,E.coli表达体系只能表达经逆转录合成的cDNA编码产物,不宜表达从基因组DNA上扩增的基因;
由于缺乏适当的翻译后加工机制,真核基因的表达产物在E.coli表达体系中往往不能被正确的折叠或糖基化修饰;
表达的蛋白质常常形成不溶性包含体,欲使其具有活性尚需进行复杂的变性-复性处理;
很难用E.coli表达体系表达大量的可溶性蛋白质。
2.真核表达体系
真核表达体系除与原核表达体系有相似之处外,一般还常有自己的特点。
构成
真核表达载体通常含有供真核细胞用的选择标记、启动子、转录和翻译终止信号、mRNA的poly(A)加尾信号或染色体整合位点等。
关于真核表达载体的基本组成见P432图23-12。
采用真核表达体系的优势
真核表达体系有酵母、昆虫、哺乳类细胞等,不仅可以表达克隆的cDNA,也可表达从真核基因组DNA扩增的基因。哺乳类细胞表达的蛋白质通常总是被适当的修饰,而且表达的蛋白质会恰当地分布在细胞内一定区域并积累。
具有转录后加工机制;
具有翻译后修饰机制;
表达的蛋白质不形成包含体(酵母除外);
表达的蛋白质不易被降解。
操作技术难、费时、费钱是其缺点。
第三节重组DNA技术在医学中的应用
目前,重组DNA技术已广泛应用于生命科学和医学研究、疾病诊断与防治、法医学鉴定、物种的修饰与改造等诸多领域,对医学临床及医学研究的影响日益增大。
一、重组DNA技术广泛应用于生物制药
利用重组DNA技术生产有应用价值的药物是当今医约发展的一个重要方向,有望成为21世纪的支柱产业之一
发展前景
利用重组DNA技术,可以让细菌、酵母等低等生物成为制药工厂,也使基因工程细菌成为各类生物基因的储藏所;可以将小鼠杂交瘤细胞人源化,让其产生人源化抗体;可以制造基因工程病毒,使病毒保留免疫原性,缺乏感染性或变成不含核酸的类病毒颗粒( virus-like- particle,VLP)。
该技术一方面可用于改造传统的制药工业,如利用该基因可改造制药所需要的工程菌种或创建新的工程菌种,从而提高抗生素、维生素、氨基酸等药物的产量
另一方面利用该技术生产有药用价值的蛋白质/多肽及疫苗抗原等产品,重组人胰岛素是利用该技术生产的世界上第一个基因工程产品
目前上市的基因工程药物已百种以上,P437表23-4中仅列出部分药物和疫苗。
二、重组DNA技术是医学研究的重要技术平台
重组DNA技术可用于医学研究的很多方面,诸如遗传修饰动物模型的建立、遗传修饰细胞模型的建立、基因获得或丧失对生物功能的影响等。
1.遗传修饰动物模型的医用研究
重组DNA技术可用于遗传修饰动物模型的研制,从而建立人类疾病的动物模型
目前已经建立了诸多人类疾病的遗传修饰动物模型,用于研究癌症、糖尿病、肥胖、心脏病、老化、关节炎等;遗传修饰猪模型的应用,可望增加从猪到人器官移植(pig to human organ transplantation)的成功率;改造蚊子的基因组,使其产生对疟疾的免疫反应,可望消灭疟疾。
2.遗传修饰细胞模型在医学研究中的应用
重组DNA技术也可用于遗传修饰细胞模型的建立,从而用于基因替代治疗/靶向治疗,或体内示踪。
体细胞基因治疗( somatic gene therapy)已经在X-连锁联合免疫缺陷病(X -linked SCID)、慢性淋巴细胞白血病( chronic lymphocytic leukemia,CLL)和帕金森病进行了临床研究,这是在人体上进行遗传工程的研究。改造T淋巴细胞,让其携带嵌合抗原受体( chimeric antigen receptor,CAR),从而达到靶向治疗疾病的CAR-T细胞也是采用重组DNA技术实现的。例如,人T细胞经基因操作成为靶向CD19的CAR-T,用于治疗难治性慢性B淋巴瘤。将绿色荧光蛋白( green fluorescent protein,GFP)与细胞内的某些蛋白相融合,可使细胞变成具有踪作用的发光细胞。
3.基因及基因功能的获得及丧失的研究
一般可通过基因的获得如转基因)或丧失(如基因敲除)进行研究,也可通过示踪实验(如GFP融合蛋白)研究基因表达产物的定位或相互作用信息等,或通过报告基因(如GFP或催化特定底物的酶)与不同启动子相融合的方法实现对基因表达调控的研究。
基因工程生物或细胞模型可用来发现一些基因的新功能,或发现新基因
三、重组DNA技术是基因及其表达产物研究的技术基础
重组DNA技术已经成为基因或基因功能获得或丧失研究的技术基础,也是基因表达产物相互作用研究的技术基础
1.在基因组水平上干预基因
重组DNA技术是基因打靶(包括基因敲除和基因敲入)及基因组编辑等的技术基础
例如,基因敲除( gene knock--out),传统的方法是利用同源重组的原理,用目的基因替换基因组上的特定基因,要实现这一目标,需要将目的基因克隆到合适的载体上,并在其两侧加上待敲除基因上的部分序列,使重组DNA进入细胞后能通过同源重组替换基因组的目标基因。条件性基因打靶( conditional gene targeting)是在目的基因两侧构建了Cre重组酶的切割位点。基因组编辑(genome editing)是指一类能定向地在基因组上改变基因序列的技术,其中 CRISPR/Cas9系统是目前应用最多的、脱靶最少的基因组编辑技术,也是细抵抗病毒感染的一种获得性免疫机制。利用 CRISPR/Cas9基因组编辑技术对特定基因进行改造,也需要在体外构建含导向crRNA( guide crRNA, gcrRNA)和Cas9编码基因的重组载体,然后将这种重组载体导入受体细胞,才能实现在基因组水平定向地改变特定基因的目的。
2.在RNA水平上干预基因的功能
RNA干扰( RNAi)是通过干扰小RNA(siRNA)与靶RNA结合,从而阻止基因表达的方法。
siRNA可以直接采用化学法合成,也可以利用DNA克隆技术构建干扰小发夹RNA,即将编码 siRNA反向互补序列和间隔序列( linker)克隆入合适的载体,在细胞内转录合成干扰小发夹RNA,实现RNA干扰目的。
3.研究蛋白质的相互作用
重组DNA技术也是蛋白质相互作用研究的技术基础。
例如,酵母双杂交系统(yeast two-hybrid- system)是利用分别克隆转录因子DNA结合结构域( DNA binding domain,DBD)和转录激活结构域( transcription activating domain,TAD)的融合基因,对DBD-融合蛋白和TAD-融合蛋白的融合部分的潜在相互作用能力进行研究。